
从研究生到博士,再到参加工作后的讲师、副教授、教授,科研人员整个科研生涯都要和论文打交道。每当我们看到别人的高分论文,总会鼓励自己:“咬咬牙,坚持下,下个高分文章就是自己”。那么,除了鼓励,我们该如何具体实现我们的小目标呢?今天,小编就结合“紫萍”基因组,与您深入探讨10分基因组文章的研究思路,以此来助力我们“10分基因组文章”小目标的完成。
01-突出 “实验材料”的研究价值
随着城市化进程的加快,地球上淡水资源逐渐减少,而紫萍(Spirodela polyrhiza)可为清洁和回收淡水资源提供生态学基础。此外,紫萍还具有分布范围广、适应强等特点,其还可作为高蛋白动物饲料、生物燃料等。因此,以紫萍为研究材料,除了有生物学价值,更有生态价值和经济价值。
02-强调论文研究的“关键点”
针对水生植物紫萍极强的环境适应性,研究者由此想到两个科学问题“紫萍的根系结构是如何进化以适应其水生生活?”、“紫萍是如何抵抗水中的病原体和致病微生物?”。
为了回答上述两个科学问题,研究者首先构建一套高质量的紫萍参考基因组,随后又设计相对应的实验来深入探究上述问题。研究者的整体研究思路如下:

图1 研究技术路线
03-构建高质量的参考基因组
已有紫萍参考基因组(Sp7498V2)是基于二代短读长测序组装的,其存在诸多短片段并导致相应序列缺失。研究者采用PacBio对紫萍进行测序,总测序深度为126×。研究者利用Falcon 和Canu软件,共组装得到411个contig,其contig N50为831 kb。随后通过BAC-末端测序(BES)将contig组装到scaffold水平,其scaffold N50为3.3Mb。最后整合已发表的二代紫萍基因组为参考,将紫萍基因组挂载到20条染色体上。通过fosmid序列评估,发现紫萍基因组序列一致性超过98.6%。
表1 紫萍组装统计结果

利用De novo预测和cDNA数据,研究者注释得到18708个蛋白编码基因。此外,与Sp7498V2相比,研究者构建的Sp7498V3基因组注释结果更好,基因长度更长、外显子数目更多。通过BUSCO评估,Sp7498V3同源蛋白的完整性(86%)也要高于Sp7498V2,表明研究者构建的紫萍基因组组装和注释结果质量更好。
最后,相比于Sp7498V2鉴定到17.3%的重复序列,研究者在Sp7498V3鉴定到重复序列占比为30.91%,且其中18.61%为长末端重复(LTR)反转录转座子,并在此基础上鉴定得到更多的嵌套LTR区间。
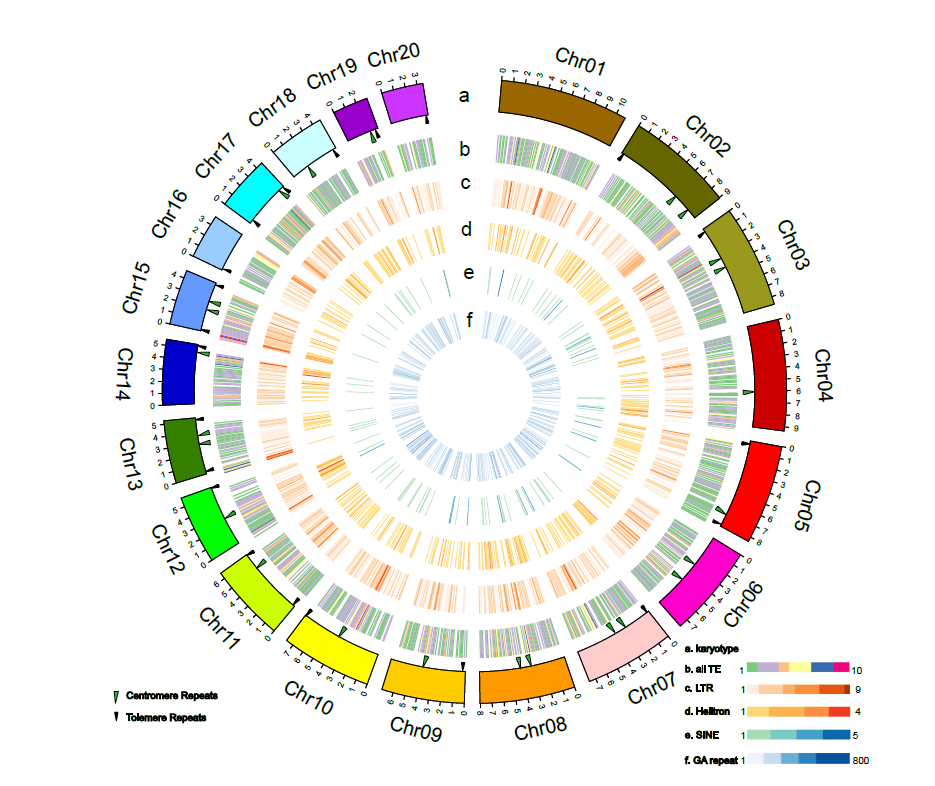
图2 重复序列的分布
04-“重点”回答论文中的生物学问题
高质量的紫萍参考基因组构建完成后,研究者对自己提出的科学问题进行了深入的研究,包括紫萍的比较基因组学分析、根系的进化历程、抗病基因的变化等。
(1)紫萍的比较基因组学分析
基于单拷贝序列,从包含大叶藻、玉米、拟南芥在内的9个近缘物种中,研究者鉴定出紫萍与大叶藻的亲缘关系最近。此外,紫萍与其它陆地单子叶植物的分化时间大约是130.4~ 140.4 MYA之间。基因家族聚类显示,紫萍与大叶藻、玉米、水稻、拟南芥共有基因为7647个,而在大叶藻中丢失了674个基因。
GO富集分析表明,在大叶藻中丢失的基因主要富集在气孔发育调节、DNA修复调节、色氨酸合成等一系列通路中。大叶藻失去的功能与其不需要应对强的紫外线、不需要利用气孔交换气体的习性相一致。与之相对应的是,与水稻、玉米和拟南芥相比,在大叶藻和紫萍中丢失了420个基因,GO富集显示这些丢失的基因主要富集在次生代谢物的生物合成和代谢通路中,这些次级代谢物在植物抵抗重力和应对干旱中发挥着重要的作用。基于此,研究者猜想由于紫萍和大叶藻为水生生活,因此它们不需要复杂的代谢物来应对温度、光照和养分的变化。

图3 紫萍与其近缘种的基因家族分析
(2)紫萍根系的进化
紫萍和陆生植物的主要区别在于水分和营养的摄取途径。与陆生植物相比,紫萍并不需要完全依赖根系吸收营养,被液体包围的组织可替代完成根的营养吸收,这导致紫萍根系结构的退化。从根组织细胞学观察、根发育相关基因挖掘和根系营养元素吸收能力研究等方面证明了紫萍的根系主要是不定根且功能发生明显的退化。

图4 紫萍根系的解剖学研究
(3)紫萍重复序列上的抗病基因
编码抗微生物肽(AMP)和蛋白的基因在紫萍的串联重复序列中显著富集,其中108个AMP基因中有92个串联重复,最多的达到22个拷贝。此外,92个串联的AMP基因,有62个得到来自全长cDNA的支持。结合转录组数据表明,紫萍中有36个串联重复的基因表达高于中等水平。总的来说,抗病基因在紫萍中串联重复扩增而且组成型表达,这与紫萍中24nt siRNA低水平的表达是相一致的。此外,与陆生植物相比,紫萍在减数分裂中不需要过多的抑制逆转录的发生,这也是为了抑制其免疫系统。

总 结
通过深入分析,我们不难看出,此篇紫萍基因组文章实验设计严谨,研究思路清晰。通过三代测序构建了紫萍高质量的参考基因组;通过比较基因组分析阐述了紫萍的起源进化历程;通过多组学分析阐述了紫萍根系和串联重复抗病基因的变化,该研究可为其他藻类植物基因组的研究提供模板思路与方法基础。
 微信公众号
微信公众号
