
“苜蓿来西或,蒲萄亦既随”,拥有两千多年栽培史的苜蓿是世界上栽培面积最广、品质最优的牧草,是真正的“牧草之王”,具有极高的生态、经济与产业价值。从分类学上讲,苜蓿是苜蓿属(Medicago)植物的统称,常见的品种包括紫花苜蓿(Medicago sativa )、蒺藜苜蓿(Medicago truncatula)、南苜蓿(Medicago polymorpha)、早花苜蓿(Medicago praecox)、小苜蓿(Medicago minima)、天蓝苜蓿(Medicago lupulina)、褐斑苜蓿(Medicago arabica)、花苜蓿(Medicago ruthenica)等,其中尤以紫花苜蓿最为出名。

图1 不同苜蓿品种的花
通过查阅各大数据库及Plant Genomes(https://plabipd.de/plant_genomes_pa.ep),共获取与苜蓿基因组学相关文献8篇,包括Nature、NC、NP、MP等顶级期刊,涉及到的品种包括蒺藜苜蓿、紫花苜蓿、南苜蓿等。基于此,小编将苜蓿基因组研究的最新进展总结如下。
01
蒺藜苜蓿(Medicago truncatula)
因倍性简单(2n=16)、基因组小、生长周期短,蒺藜苜蓿一直被作为豆科—根瘤菌共生遗传学与进化的模式植物,也是第一个被测序发表的苜蓿品种。蒺藜苜蓿基因组前后历经三个版本,涉及到4篇文章,具体总结如下。
1.蒺藜苜蓿草图-Nature
(Mt 3.50)
文章题目:The Medicago genome provides insight into the evolution of rhizobial symbioses
发表时间:2011年11月
测序策略:BAC+Illumina+BioNano
主要结果:
蒺藜苜蓿是紫花苜蓿的近缘种,因多种特性成为研究共生机制的模式植物。研究者利用BAC+Illumina+BioNano策略,构建了蒺藜苜蓿Mt 3.5版本的参考基因组。其基因组大小为375Mb,实验支持的编码蛋白基因为47845个,基因的平均长度为2211bp。考虑到WGD对植物进化的重要性,研究者利用WGD分析、转录组验证,研究了WGD事件对蒺藜苜蓿与根瘤菌共生的影响,指出早期WGD促进了NFP、Ern1等转录因子的形成,允许Nod因子信号中关键成分的出现进而使根瘤菌形成复杂的结瘤。总之,WGD对蒺藜苜蓿与根瘤菌的共生起到了至关重要的作用。
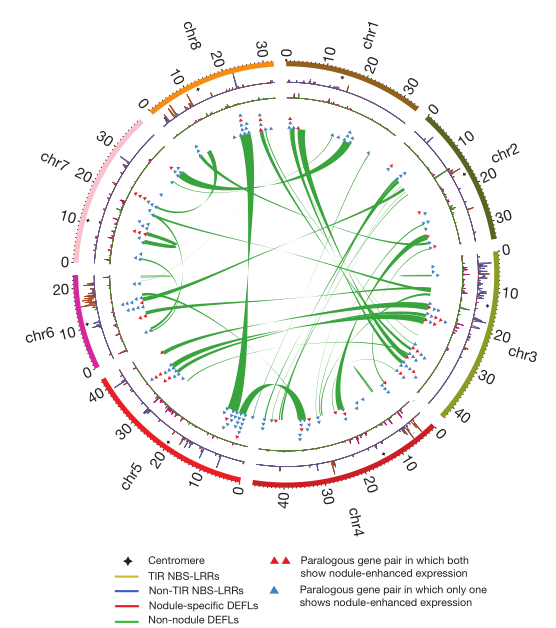
图2 蒺藜苜蓿的WGD事件及选择的基因(circos图)
2.蒺藜苜蓿精细图-两篇BMC Genomics
(Mt 4.0)
文章题目:An improved genome release (version Mt4.0) forthe model legume Medicago truncatula;
Strategies for optimizing BioNano and Dovetail explored through a second reference quality assembly for the legume model, Medicago truncatula
发表时间:2014年4月;2017年8月
测序策略:454+Illumina+GBS+ BioNano;Illumina(71.4×)+PacBio(107×)+Chicago+BioNano
主要结果:
2011年发表的蒺藜苜蓿Mt 3.5版本基因组主要是依据BAC测序来完成的,在此基础上,2014年和2017年研究人员分别对Mt 3.5进行升级到Mt 4.0。在第一篇文章中,研究者运用WGS测序配合GBS和BioNano,将蒺藜苜蓿的染色体挂载率提高到93%,并通过多种注释方法预测得到50894基因,最后研究者构建了数据库,将Mt 4.0的组装与注释信息进行共享。

图3 蒺藜苜蓿基因组4.0版本与3.5版本染色体挂载比较
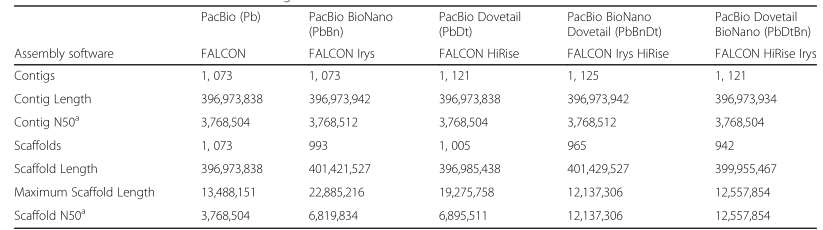
第二篇文章中,研究者第一次使用了三代测序数据(PacBio)来组装蒺藜苜蓿基因组(R108),并结合BioNano和Chicago辅助组装技术,设置了五种组装策略,来系统评估三代测序和辅助组装技术联合使用在提升植物基因组组装质量中的适用性。结果表明,在5种组装策略中,PacBio+Chicago+Bionano组装结果的连续性最好(Scaffold N50=12.55Mb),准确性最高;并鉴定出了22.7Mb的新序列。
表1 不同策略组装的蒺藜苜蓿基因组装结果比较
3.最完整的蒺藜苜蓿基因组-Nature Plants
(Mt 5.0)
文章题目:Whole-genome landscape of Medicago truncatula symbiotic genes
发表时间:2018年11月
测序策略:BAC+ Illumina +PacBio+BioNano
主要结果:
测序技术的突破促进了真核生物基因组功能结构的破译,使研究人员可以对基因表达进行更全面和更细致的分析。本研究中,研究者使用多种组装策略,获得了迄今为止最完整的蒺藜苜蓿基因组(Mt 5.0),基因组大小为430Mb,Scaffold N50=56.23Mb。对Mt 5.0进行注释可以更全面分析转座子及其动态,并鉴定共生机制新的参与者,特别是1037个上调的长非编码RNAs (lncRNAs)。研究者还发现,在共生体中上调或在结核分化区表达的大部分基因(分别约为35%和38%)在基因组簇中可以共定位(分别为270和211),称之为共生岛。这些共定位区域包含大量表达的lncRNA基因,并显示差异的DNA甲基化和组蛋白标记。因此,表观调控和lncRNA是蒺藜苜蓿基因组中共生基因共表达的有力调控元件。
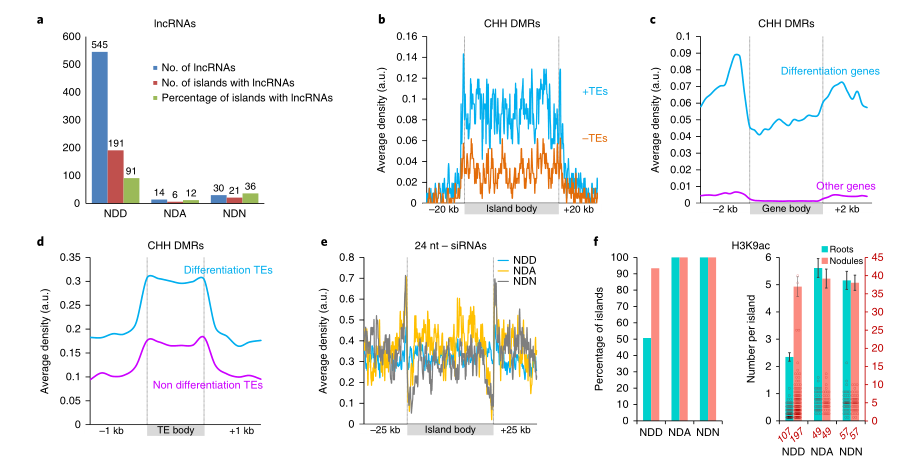
图4 蒺藜苜蓿共生基因表达的潜在调控元件
02
紫花苜蓿(Medicago sativa)
紫花苜蓿为同源四倍体(2n=4x=32)且基因组较大(4c=3.2Gb),在测序技术昂贵的年代,组装其基因组是异常困难的事情。而随着三代测序技术的逐渐成熟,紫花苜蓿四倍体、二倍体及单套基因组在2020年被陆续破译,相关成果发表在NC、MP、HR上,具体情况总结如下。
1.四倍体紫花苜蓿基因组分型-NC
文章题目:Allele-aware chromosome-level genome assembly and efficient transgene-free genome editing for the autotetraploid cultivated alfalfa
发表时间:2020年5月
测序策略:HiFi(22×)+ONT+Illumina(40×)+Hi-C(118×)
主要结果:
利用高准确性的HiFi Reads,同时结合ALLHi-C算法,研究者构建的紫花苜蓿基因组大小为3.15Gb,Contig N50=459 Kb,并最终将四倍体基因组组装到了32条染色体上。对四套染色体进行系统比较,表明四套等位染色体的大小、基因数据、重复元件均高度相似,共线性关系和Ka/Ks比例都高度保守,这说明研究者构建了超高质量的紫花苜蓿分型图谱。随后,研究者进一步开发了基于CRISPR/Cas9的基因编辑技术体系,培育了一批多叶型紫花苜蓿材料,其杂交后代表现出稳定的多叶型性状且不含转基因标记,从而证实了栽培苜蓿基因编辑体系高效且易于实施,可大大加速紫花苜蓿的育种速度。
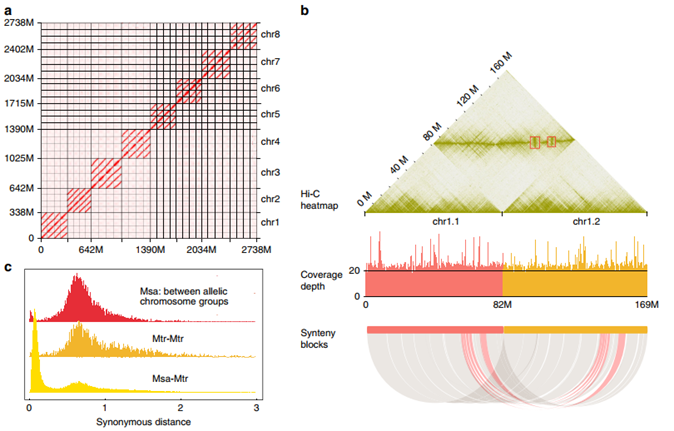
图5 紫花苜蓿同源染色体间的组装与比较
2.紫花苜蓿基因组+GWAS分析-MP
文章题目:The Chromosome-Level Genome Sequence of the Autotetraploid Alfalfa and Resequencing of Core Germplasms Provide Genomic Resources for Alfalfa Research
发表时间:2020年7月
测序策略:PacBio+Hi-C+Illumina+Bionano
主要结果:
基于多种组装技术,研究者构建了紫花苜蓿栽培种“中苜1号”高质量的单套基因组(基因组大小816Mb,Contig N50=3.92Mb),注释得到49165个基因。随后,研究者对137份紫花苜蓿核心种质及25份可能的祖先种进行重测序,群体结构分析表明紫花苜蓿分为3个Group,Group1以蓝花苜蓿为主,Group 2 可能包含未知亚种,Group 3以四倍体紫花苜蓿为主(可进一步分为三个亚群,与地理位置高度相关);结合历史事件,研究者推断栽培紫花苜蓿起源于欧洲的一个祖先群体,而北美和南美的群体分别由来自欧洲的两批殖民者携带过来。最后,研究者对137份紫花苜蓿的30多个农艺性状进行GWAS分析,关联到了100个候选区域,并通过多种方法验证MsFTa2基因的表达差异可能影响紫花苜蓿的秋眠和耐盐性,并有助于提高紫花苜蓿的环境适应性。
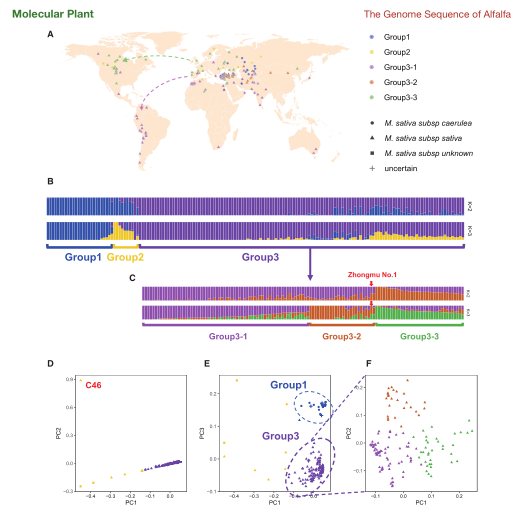
图6 162份紫花苜蓿的群体结构分析
3.二倍体紫花苜蓿基因组-HR
文章题目:A chromosome-scale genome assembly of a diploid alfalfa, the progenitor of autotetraploid alfalfa
发表时间:2020年12月
测序策略:ONT+Hi-C+Illumina
主要结果:
紫花苜蓿是一种重要且广泛种植的饲料作物,也被用作蔬菜和药材。基于ONT、Hi-C、Illumina测序,研究者构建了二倍体紫花苜蓿的参考基因组,其基因组大小为793.2Mb,Contig N50=3.86Mb,注释得到47202个蛋白编码基因。与蒺藜苜蓿相比,二倍体紫花苜蓿基因组几乎大两倍,主要是由更大的基因家族和更多的重复元件引起的,而不是WGD事件。比较基因组分析表明,蒺藜苜蓿和紫花苜蓿在520万年前从共同祖先中分化出来,随后发生了染色体重排与融合。最后,研究者在二倍体紫花苜蓿中鉴定到了489个抗性基因和一些参与木质素与纤维合成相关的候选基因。
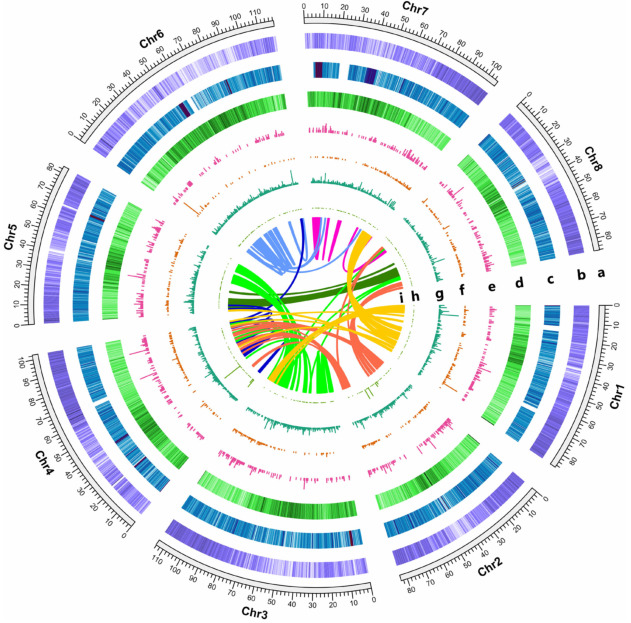
图7 二倍体紫花苜蓿基因组特征
03
南苜蓿(Medicago polymorpha)
文章题目:The genome of Medicago polymorpha provides insights into its edibility and nutritional value as avegetable and forage legume
发表期刊:Horticulture Research
发表时间:2021年3月
测序策略:PacBio+Hi-C+Illumina
主要结果:
南苜蓿是一种营养可口的饲料和蔬菜作物。本研究中,研究者利用PacBio、Hi-C和Illumina测序构建了南苜蓿染色体水平参考基因组,其基因组大小为457.53Mb,Scaffold N50=55.72Mb,92.92%的序列被锚定到7条染色体上。比较基因组分析表明,与光合作用相关的基因在南苜蓿中扩张,与木质素生物合成的基因发生了收缩。代谢组结果表明,南苜蓿中富集了大量的黄酮类化合物、维生素、生物碱及萜类化合物,这表明南苜蓿木质素含量降低但营养价值很高。总之,本研究为南苜蓿的遗传育种提供了新见解。
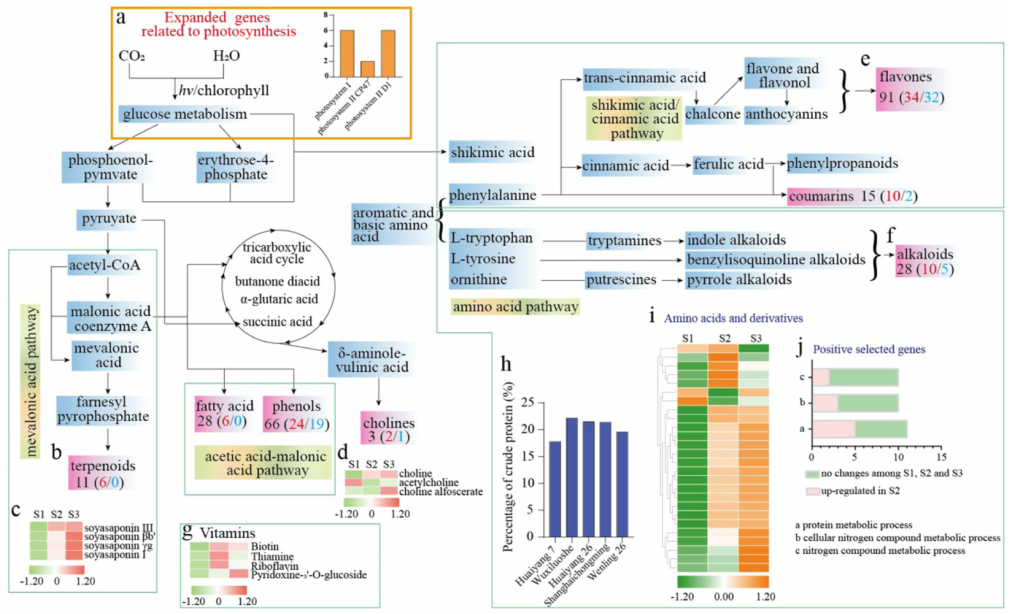
图8 南苜蓿氮固定的调控网络
总结
作为集饲料、食物、药材为一体的苜蓿,多年来始终是科研人员热捧的“明星物种”。伴随着测序技术的不断进步,苜蓿基因组学先后解决了苜蓿基因组结构、起源进化、固氮共生、农艺性状定位、分子育种等一系列基础生物学问题,为苜蓿乃至牧草行业的绿色、稳产、高品的发展提供了新见解与新方向。展望未来,我们认为苜蓿基因组学的焦点与突破点将集中在以下3个方面:
(1)苜蓿属的泛基因组分析(构建多品种的基因组、寻找不同品种间的PAV等)
(2)苜蓿生理形态的解析(多组学解析固氮共生、抗逆、叶型等)
(3)苜蓿新品种的选育(GWAS+QTL定位关键基因、表观多组学寻找调控元件、基因编辑体系构建等)
“天寒苜蓿芽未茁”, 愿在基因组学的助力下,苜蓿不再成为我国农业领域的“卡脖子”问题!
参考文献:
[1] Young N D, Debellé F, Oldroyd G E D, et al. The Medicago genome provides insight into the evolution of rhizobial symbioses[J]. Nature, 2011, 480(7378): 520-524.
[2] Tang H, Krishnakumar V, Bidwell S, et al. An improved genome release (version Mt4. 0) for the model legume Medicago truncatula[J]. BMC genomics, 2014, 15(1): 1-14.
[3] Moll K M, Zhou P, Ramaraj T, et al. Strategies for optimizing BioNano and Dovetail explored through a second reference quality assembly for the legume model, Medicago truncatula[J]. BMC genomics, 2017, 18(1): 1-16.
[4] Pecrix Y, Staton S E, Sallet E, et al. Whole-genome landscape of Medicago truncatula symbiotic genes[J]. Nature Plants, 2018, 4(12): 1017-1025.
[5] Chen H, Zeng Y, Yang Y, et al. Allele-aware chromosome-level genome assembly and efficient transgene-free genome editing for the autotetraploid cultivated alfalfa[J]. Nature communications, 2020, 11(1): 1-11.
[6] Shen C, Du H, Chen Z, et al. The Chromosome-level genome sequence of the autotetraploid alfalfa and resequencing of core germplasms provide genomic resources for alfalfa research[J]. Molecular Plant, 2020, 13(9): 1250-1261.
[7] Li A, Liu A, Du X, et al. A chromosome-scale genome assembly of a diploid alfalfa, the progenitor of autotetraploid alfalfa[J]. Horticulture research, 2020, 7(1): 1-12.
[8] Cui J, Lu Z, Wang T, et al. The genome of Medicago polymorpha provides insights into its edibility and nutritional value as a vegetable and forage legume[J]. Horticulture research, 2021, 8(1): 1-12.
 微信公众号
微信公众号
