
青霉菌广泛分布于陆地和海洋等各种自然环境中,其中草酸青霉可分泌大量的碳水化合物活性酶(CAZymes)来消化植物生物量,并产生具有多种生物活性的次级代谢物,包括抗菌和抗肿瘤化合物,在生物炼制、生物修复和制药行业有极大的应用潜力。从中国亚热带森林土壤中分离得到的草酸青霉菌株HP7-1能产生高活性的纤维素酶,可用于预处理过的甘蔗渣,将木质纤维素转化为葡萄糖,再发酵生产燃料乙醇,因此具有良好的工业应用潜力。然而,目前已测序的六株草酸青霉菌株(114-2、HP7-1、SYJ-1、JU-A10-T、TY02和SGAir0226)的基因组序列均不足以达到分析染色质三维结构的要求,难以研究染色质的空间结构在细胞功能和基因表达调控中起着何种重要作用。
近日,广西大学赵帅研究组联合永利集团3044解析了丝状真菌草酸青霉菌株HP7-1的三维基因组图谱,研究成果以“Three-Dimensional Genome Map of the Filamentous FungusPenicillium oxalicum”为题发表在微生物学知名期刊Microbiology Spectrum(IF:7.171),该研究采用PacBio测序技术和Hi-C技术,构建了草酸青霉菌株HP7-1的高质量染色体水平基因组序列,并分析了染色质三维结构,检测到1099个TAD/globule结构(2kb~76kb),在globule边界富集出了转录因子motif。在1kb高分辨率下检测到12203个顺式互作和7884个反式互作,分析了纤维素酶和木聚糖酶基因以及转录因子编码基因的空间互作。永利集团3044承担了该研究中的Hi-C建库、测序和部分分析工作。

材料方法
研究材料:草酸青霉菌株HP7-1
研究方法:Pacbio测序、Hi-C技术
研究结果
1.草酸青霉基因组
该研究采用Pacbio测序技术和Hi-C技术组装得到高质量、大小为30.79Mb的草酸青霉基因组。contig N50达3.81Mb,scaffold N50为4.07Mb,拼接成的8条染色体大小为1.80~5.87Mb,BUSCO评估其完整性为98.60%,注释得到9728个蛋白编码基因,鉴定到了85个新的蛋白质。在9728个蛋白质中,有712个CAZymes、496个转录因子和47个与次级代谢相关的蛋白簇。除此以外,还注释得到45个rRNA和201个tRNA。
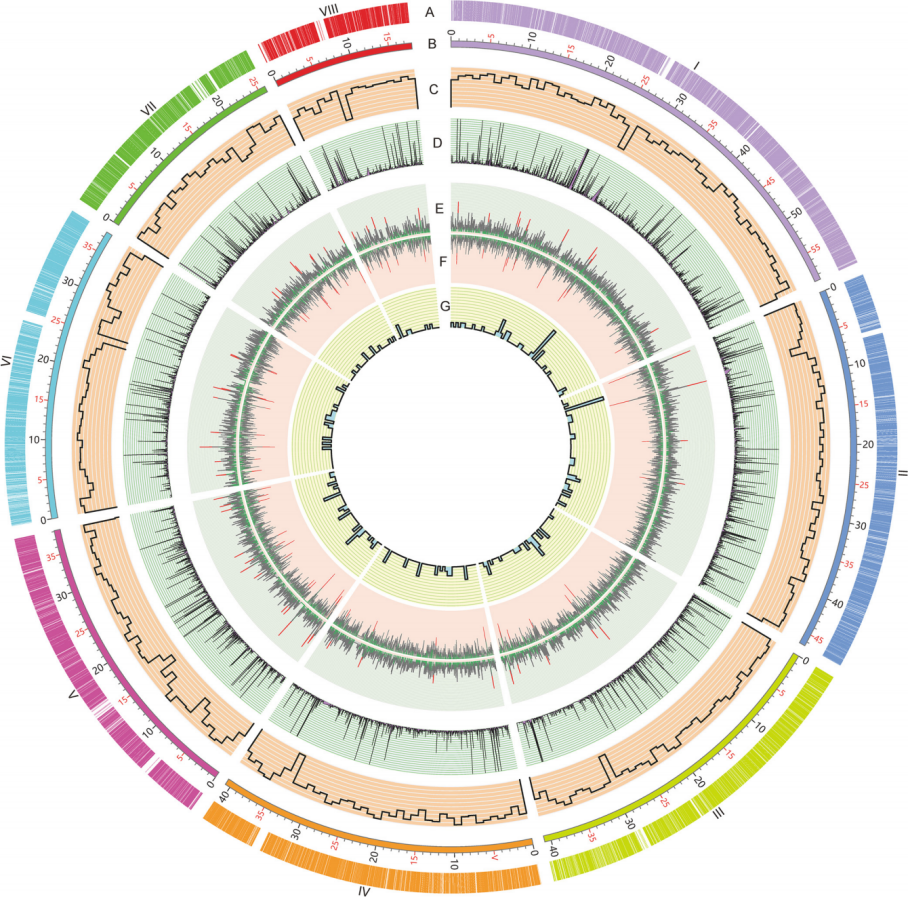
图1.草酸青霉基因组特征
2.草酸青霉三维基因组
基于Hi-C互作数据观察1kb、2kb、10kb和20kb分辨率下的草酸青霉三维基因组结构。除了明显的染色体内的互作频率高于染色体之间的互作,草酸青霉中无论是在所有8条染色体内还是在染色体之间,着丝粒周围(包含着丝粒)和亚端粒区域(包含端粒)之间存在显著高频互作,表明草酸青霉的三维染色质结构属于I型具有类似Rabl构象的着丝粒聚类特征。
在1kb分辨率下鉴定出12203个顺式和7884个反式显著互作,它们之中分别含有5738个和1324个基因。顺式互作基因的30.7%参与代谢,其次是遗传信息处理(8.5%)和细胞过程(6.6%),而反式互作基因的33.3%参与代谢。另外,反式互作的基因更加明显的参与了核苷酸和能量代谢,顺式互作的基因则更偏向于异种生物的生物降解和代谢。
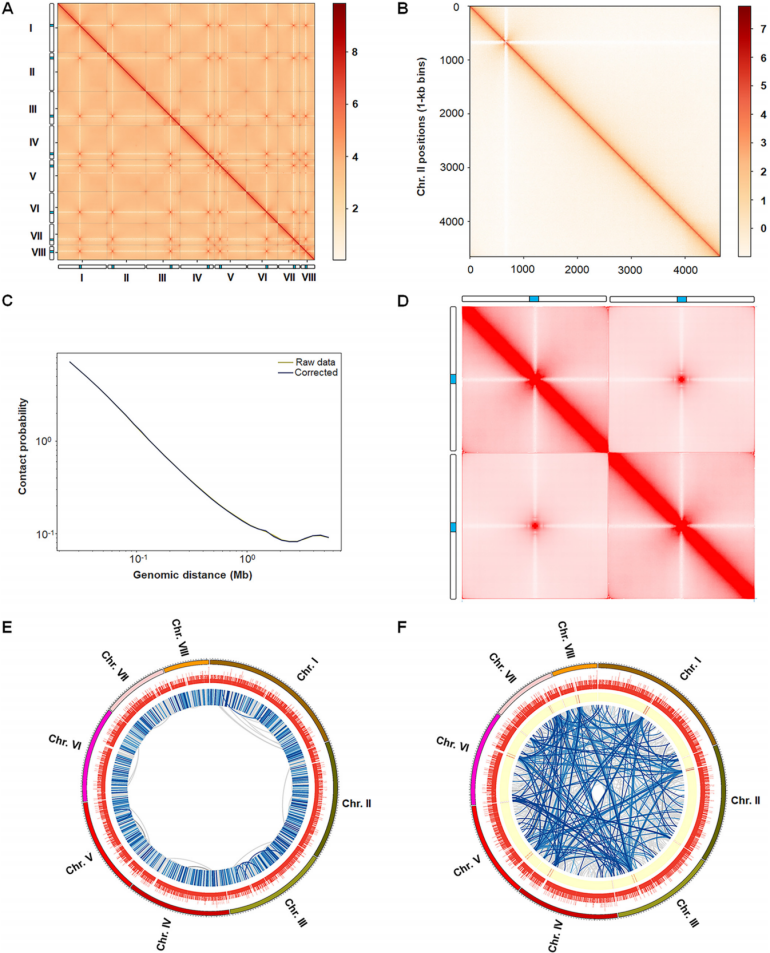
图2.草酸青霉的全基因组空间互作图谱
哺乳动物和植物中的“TAD”结构,在一些真菌中被称为“globule”结构,大小在50kb到100kb之间。在2kb分辨率下,同样基于insulation score方法,在草酸青霉中检测到了1099个globule(2~76kb)。其边界和内部分别有1282和9476个基因,其中1051个基因同时位于globule边界和内部,主要参与代谢(32.06%),其次是遗传信息处理(9.9%)和细胞过程(6.7%)。
对草酸青霉的基因组结构进行3D建模,得到一个类似“灯泡”的染色体构象,所有的着丝粒都聚集在一端,而端粒几乎聚集在另一端。

图3.草酸青霉基因组的3D结构模型
3.草酸青霉中纤维素酶和木聚糖酶基因,以及转录因子编码基因的空间互作
在草酸青霉基因组注释结果中,有25个纤维素酶和10个endo-β-1,4-木聚糖酶(XYN)基因,不均匀地分布在八条染色体上。主要的纤维二糖水解酶基因位于四号染色体上。除了七个基因,大部分纤维素酶和XYN基因分布在不同的globule。在所有纤维素酶和木聚糖酶基因中,15个具有顺式互作,6个具有顺式和反式互作,与这些基因发生顺式互作的DNA片段是每个基因的邻近上游和下游侧翼区域,例如启动子区和终止子区。β-葡萄糖苷酶基因POX_g08536与多个片段存在反式互作,这些反式相互作用可能是由于着丝粒和端粒的整体基因组接近造成的,也可能是对特定碳源Avicel的诱导反应或通过接近和诱导的共同作用所致。结合在Avicel碳源下草酸青霉的主要纤维素酶和木聚糖酶基因共表达但DNA低频互作的现象,作者猜测纤维素酶和木聚糖酶的生物合成有条件且被特异性控制,而转录因子(TF)介导的转录过程则可能与此相关。
在该研究中,496个TF分布在430个globule内,其中77个TF基因的部分DNA序列在globule边界。346和79个TF基因分别发生有顺式和反式互作,64个TF基因同时发生这两种互作。对于调控纤维素酶和木聚糖酶基因表达的关键转录因子的编码基因,会在非优选碳源(包括Avicel)时有不同程度的转录,并且其中几乎所有基因都与相邻的上、下侧翼区域存在顺式相互作用。与纤维素酶和木聚糖酶基因的相互作用相比,涉及TF的编码基因的相互作用并不频繁。
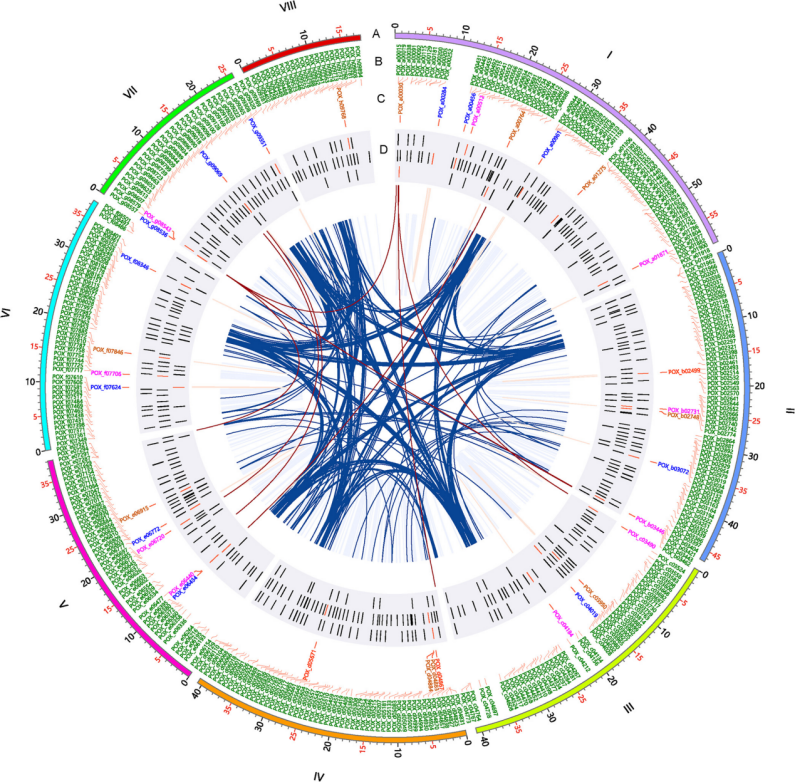
图4.草酸青霉中纤维素酶和木聚糖酶基因,以及转录因子编码基因的空间互作
4.globule边界的转录因子motif富集
本研究利用JASPAR数据库中的真菌TF-binding profile,选择MEME Suite对草酸青霉菌株HP7-1的globule边界区域进行motif扫描,共检测到163个候选motif。基于globule边界的TF motif分析,前三个显著富集的是POX_c04470、POX_c04124和POX_b02187蛋白。NCBI BLASTP鉴定出它们是AZF1、SPT23和SFL1的同源蛋白,将其重命名为PoxAZF1、PoxSPT23和PoxSFL1。MEME Suite扫描显示,PoxAZF1 TF结合在多个纤维素酶基因启动子区(1.5 kb上游),PoxSPT23和PoxSFL1 TF则是结合到主要纤维素酶和木聚糖酶基因的启动子。
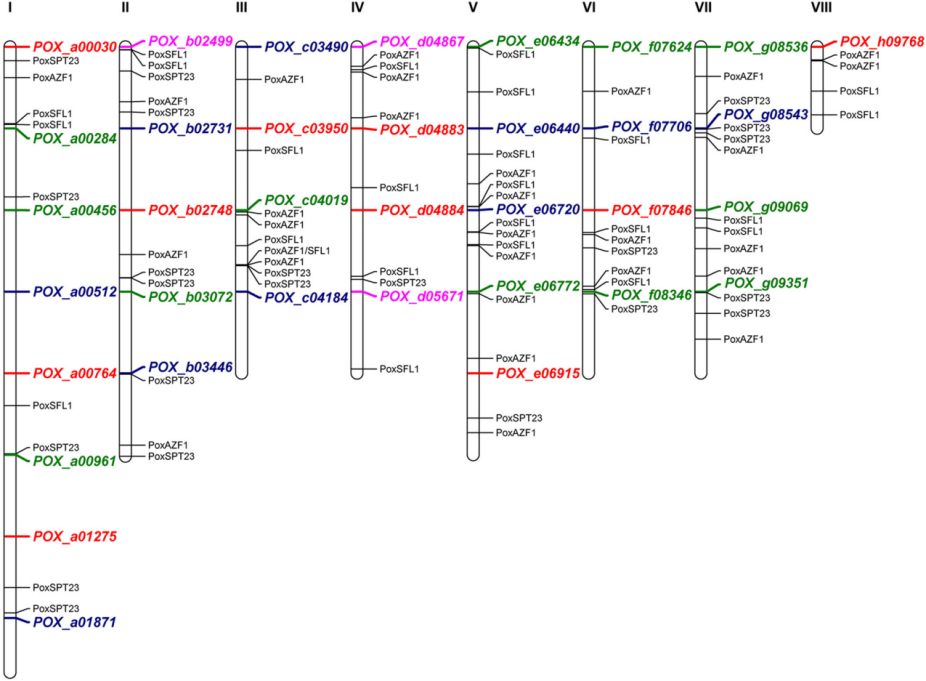
图5.PoxAZF1、PoxSFL1和PoxSPT23 TF在纤维素酶和木聚糖酶基因启动子区的motif富集
总 结
该研究首次解析出了丝状真菌草酸青霉的染色体水平基因组及其三维结构,发现着丝粒之间和端粒之间均存在高频相互作用,检测到1099个globule结构,其边界富集有许多结合转录因子的motif,如PoxAZF1、PoxSPT23和PoxSFL1。构建了草酸青霉3D基因组模型,绘制了纤维素酶和木聚糖酶基因及转录因子编码基因的空间互作。该研究为真菌染色质相互作用提供了全局视角,并为研究丝状真菌中基因表达的空间调控提供了重要资源。
广西大学赵帅副研究员为本文的通讯作者,广西大学李成喜博士为本文第一作者,永利集团3044刘琳博士署名参与了本研究。该研究得到了国家自然科学基金、广西重点研发计划项目的专项经费以及2019年广西千名中青年骨干教师培训计划的支持。
参考文献:
Li CX, Liu L, et al. Three-Dimensional Genome Map of the Filamentous Fungus Penicillium oxalicum. Microbiology Spectrum, American Society for Microbiology, 0(0): e02121-21.
 微信公众号
微信公众号
