
真核生物染色体折叠的结构已被染色体构象捕获系列技术持续深入分析,染色体构象捕获系列技术使用交联基于空间邻近连接的位点来估计接触频率,从而得到多个层级的三维染色体结构,例如compartment、TAD,以及CTCF和黏连蛋白介导的染色质loop。
用于染色质构象捕获的Hi-C技术已臻成熟,广泛应用于各大动植物和微生物。Hi-C 3.0也部署有高精度的互作信息,能检测到更多的loops和更强的compartment,并兼顾捕获短距离和长距离互作的信息。Micro-C是2015年发表的Hi-C衍生技术,其与Hi-C在实验步骤上最大的不同在于用MNase切断核小体之间的连接DNA。2016年Micro-C实验引入了双交联体系升级为Micro-C XL。永利集团3044在之前分享了Micro-C XL用于酵母的处理经验,明确了Micro-C XL的超高分辨率优势。相较于传统Hi-C,Micro-C XL可以分析核小体相关互作信息,还可以获得更精细的真核基因组空间结构。今天就以酵母和哺乳动物的相关精细结构解析为主题,一起走入Micro-C XL在真核生物的应用,领略属于Micro-C XL的技术特色。
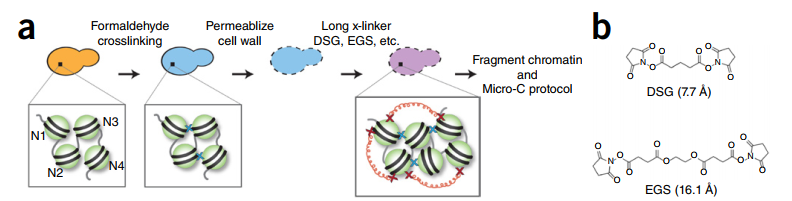
图1 Micro-C XL实验流程,增加了双交联步骤
01
静止期酵母的基因表达抑制机制

图2 文章信息
文章题目:Condensin-dependent chromatin compaction represses transcription globally during quiescence
发表期刊:Molecular Cell(IF:17.97)
发表时间:2019年2月
物种材料:对数期和静止期的酿酒酵母(Saccharomyces cerevisiae)细胞
测序方法:Micro-C XL、ChIP-seq、RNA-seq
细胞的静止状态(quiescence)是一种退出细胞周期的可逆状态,能在较长的时间内不进行分裂,因此可以维持干细胞状态,不利于肿瘤形成。相较于细胞衰老和凋亡而言,静止期细胞会诱导有助于抗逆性和长寿的通路。该研究采用Micro-C XL,在核小体分辨率下绘制全基因组范围的染色质相互作用,并且发现凝聚素(condensin)复合物结合在静止细胞整个基因组中,促进以前未识别的染色质结构域(L-CID)的边界之间loop的形成。而condensin耗尽会破坏结构域内的染色质压缩,在边界附近和全基因组结构域内解除基因抑制。因此condensin在静止期间是通过挤压loop形成来局部压缩染色质,从而抑制转录。
在该研究中,研究者首先结合已有的静止细胞RNA-seq分析,以及指数生长期和静止期的ChIP-seq(Pol II)信号,明确了静止期细胞处于转录抑制状态,辅以DAPI的DNA染色实验,确定静止期的转录抑制与染色质凝聚相关。其次,使用Micro-C XL技术以约150bp分辨率绘制短距离和长距离染色质互作,观察到静止期(Q)样较对数期(Log)而言有较多的loop结构。联合Condensin亚基Brn1的ChIP-seq,观看到Brn1在Q样本中特异性定位,并且Brn1是富集在Q样本的L-CID边界,Brn1 peaks间倾向形成loops,因此condensin在Q期样本结合L-CID边界,参与静止期样本L-CID结构边界之间loop的形成。最后,基于人成纤维细胞构建的condensin耗竭模型中PoII结合信号上升,说明Condensin对Q时期转录抑制是必须的。因此在细胞静止期,condensin在CID边界间结合形成loops且抑制基因表达。
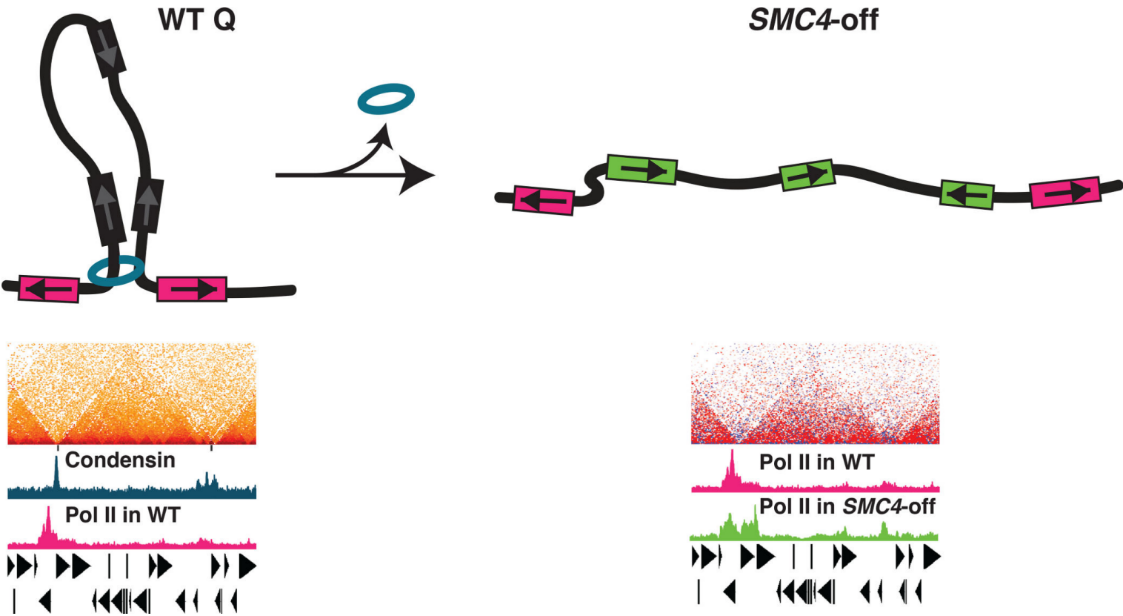
图3 condensin在静止细胞中的功能模型
02
染色质凝聚化机制

图4 文章信息
文章题目:Local chromatin fiber folding represses transcription and loop extrusion in quiescent cells
发表期刊:Elife(IF:8.14)
发表时间:2021年12月
物种材料:对数期和静止期的酿酒酵母(Saccharomyces cerevisiae)细胞
测序方法:Micro-C XL、ChIP-seq、MNase-seq
邻近核小体之间的相互作用介导的染色质纤维折叠抑制转录。然而,局部染色质纤维压缩与细胞转录之间的因果关系还有待确定。进入和退出静止状态对于维持成体干细胞和活化淋巴细胞等多种生物过程至关重要,并且与病原微生物的耐药性和癌症复发有关,并且静止期的出芽酵母经历了显著的染色质重组和转录重编程。该研究基于Micro-C XL技术,发现静止酵母中局部核小体间互作范围的增加推动了全基因组染色质丝的压缩。与积极分裂的细胞不同,静止期细胞中的核小体间相互作用需要组蛋白H4尾修饰。这种静止特异性染色质折叠全局抑制转录并抑制凝聚素挤压loop的形成。
在该研究中,静止期(Q)样较对数期(Log)酵母细胞的Micro-C XL分析发现静止期相对对数期而言n+1(相邻核小体间)互作与n+2(相隔核小体间)互作频率较低,远程互作频率较高。Micro-C XL交联步骤去掉长交联剂DSG后,Q样本变化较少,而Log样本远程互作频率更低。说明Q时期存在使较远的核小体间发生互作的机制。而且HAADF-STEM断层扫描方法显示Q期的染色质丝相对紧凑。另外结合Mnase-seq定位核小体和组蛋白ChIP-seq等方法,研究发现30nm染色质丝构成需要依赖H3与H4 N端末尾间互作,而H4K16Ac可以抑制这一作用。ChIP结果表明Q与Log的组蛋白乙酰化存在显著差异。通过组蛋白去乙酰化抑制剂TSA处理,抑制Q期的组蛋白去乙酰化后,样品的n+1与n+2间互作增强,而远程互作减弱。因此静止特异性染色质折叠和组蛋白乙酰化有关。并且基于突变体的验证实验,确定静止特异性局部染色质折叠抑制转录以及抑制凝聚素的环挤出。
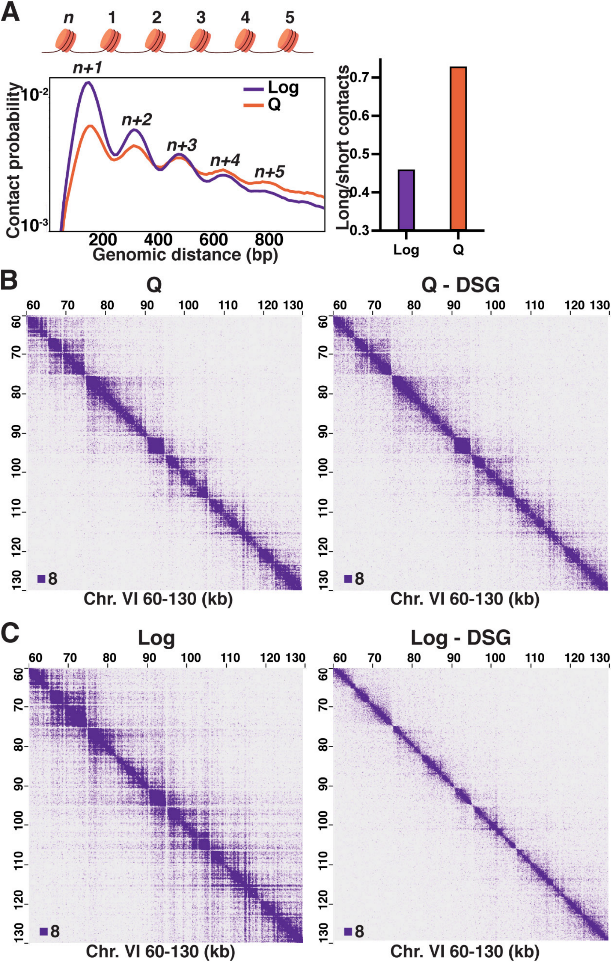
图5 对数期和静止期细胞的局部核小体间互作有差异
03
CTCF蛋白与RNA结合结构域功能

图6 文章信息
文章题目:Distinct Classes of Chromatin Loops Revealed by Deletion of an RNA-Binding Region in CTCF
发表期刊:Molecular Cell(IF:17.97)
发表时间:2019年12月
物种材料:小鼠与人细胞系
测序方法:Micro-C XL、ChIP-seq、RNA-seq
哺乳动物基因组的TAD结构由CTCF和黏连蛋白锚定的染色质环组成。一些loop特定存在于某类细胞。该研究解析了CTCF loop的建立机制是通用的还是特定于位点的。研究CTCF聚类时,研究者发现体外CTCF成对化对RNase酶敏感,并且CTCF内部的RNA结合区 (RBRi)在体内介导CTCF聚类和RNA相互作用。删除RBRi会损害小鼠胚胎干细胞中大约一半的染色质环,并导致基因表达失调。环形成的破坏会引起RBRi突变体CTCF的聚集和染色质结合减少,这会反过来不能暂停黏连蛋白介导的挤出模型。
在该研究中,通过结合基因组编辑、单分子和超分辨率成像、体外生物化学、PAR-CLIP、ChIP-seq、RNA-seq和 Micro-C XL方法综合分析确定了CTCF的RBRi的关键作用。在该研究中,CTCF的RNA结合结构域RBRi会影响部分loops,TAD,Stripes结构,并影响相关基因表达。CTCF蛋白缺失RBRi后,部分loops结构丢失,部分TAD边界丢失。compartment没有发生变化。研究确定了RBRi介导CTCF聚类,并且RBRi的丢失仅破坏CTCF介导的染色质环并影响500个基因的表达。因此CTCF边界至少可以分为两个类:依赖RBRi的和不依赖RBRi的。
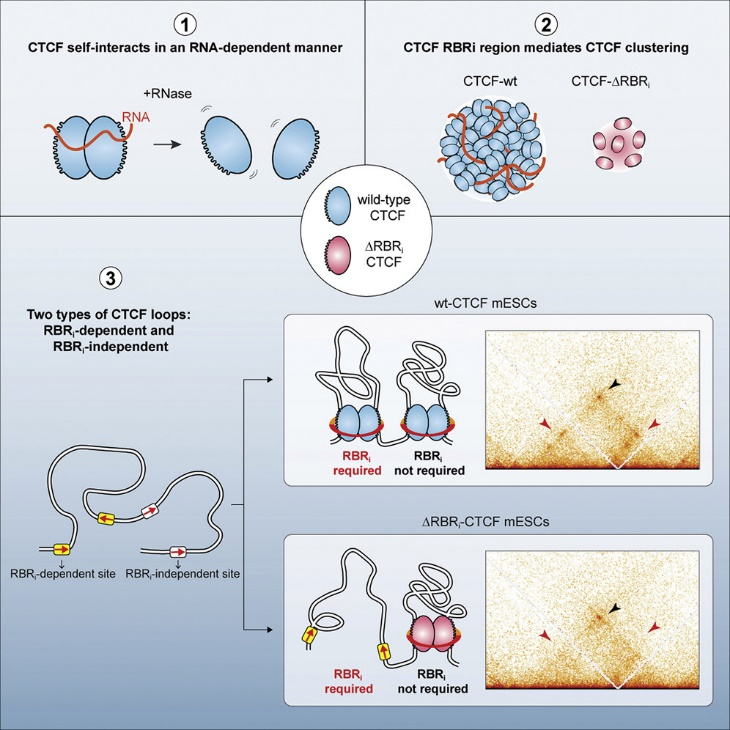
图7 RBRi介导CTCF聚类且其缺失影响染色质环
04
哺乳动物转录相关超高分辨率三维结构特征

图8 文章信息
文章题目:Resolving the 3D landscape of transcription-linked mammalian chromatin folding
发表期刊:Molecular Cell(IF:17.97)
发表时间:2020年05月
物种材料:小鼠胚胎干细胞
测序方法:Micro-C XL、ChIP-seq、MNase-seq
在哺乳动物中,1D和3D基因组图谱之间的分辨率差距以及缺乏低于TAD水平的已知染色质特征极大地限制了我们对基因调控及其与染色质结构的潜在联系的理解。这种哺乳动物的基因特异性结构和局部核小体折叠在很大程度上仍未被探索。该研究通过使用高分辨率(约200 bp)的Micro-C XL来探索小鼠胚胎干细胞的3D基因组组织和转录调控之间的联系。该研究专注于剖析TAD规模以下的染色质折叠原理,以探究转录和转录调节因子如何有助于哺乳动物染色体复杂环境中这种更精细的3D基因组结构规模。研究揭示了以前模糊不清的更精细的基因组组织,在染色质折叠和基因调控之间建立了功能联系。
在该研究中,首先基于Micro-C XL技术得到小鼠胚胎干细胞的超高分辨路互作矩阵,通过转录因子、辅因子和染色质修饰的组合分析将TAD区域在空间上分离成各种更精细的结构,这些结构具有不同的调节特征,包括stripes(对应于互作图中从对角线延伸的线,被认为是由黏连蛋白介导的loop挤压过程产生的)、loops(dots)和连接启动子与启动子 (P-P) 或增强子与启动子 (E-P) 的结构域,以及Polycomb区域之间的束触点(bundle contact)。在超高分辨率矩阵中,可以识别到promoter相关loops,stripes,domain,以及Bundle contacts等结构,转录活性的高低与promoter相关染色体空间折叠程度相关联。与Hi-C相比,Micro-C XL检测到更多的domain,loops(dot),以及stripe。并且Micro-C XL使用更小的数据量就能得到更多的loop信息。并且通过分析发现Micro-C XL数据在compartment A中可以识别到更多的domain边界,识别的结构更小。边界处富集Promoter,CpG-island。且距TSS较近。超高分辨率下,promoter相关互作可以分成多种类型(P-P、E-P)。在此基础进一步分析,发现CTCF与conhesin因子介导长距离的互作,通常构成TAD结构,而转录因子及相关因子介导短距离互作且可能与多个位点间相互作用。除此以外,从结构域边缘延伸的E-P stripe通常在没有CTCF和cohesin占位的情况下主要连接共同表达的基因座。转录活性与局部染色质折叠强度相关联,转录抑制剂处理会影响Pol II介导的染色质折叠,对较大尺度折叠影响甚微,因此转录的急性抑制会破坏这些基因相关的折叠特征,而不会改变高级染色质结构。
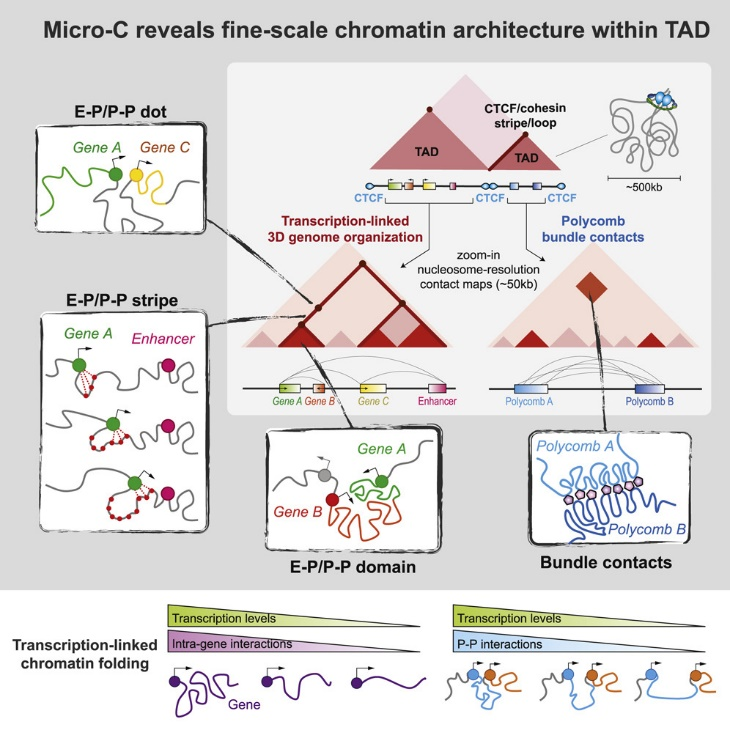
图9 精细三维结构与基因转录关系
文末福利
永利集团3044公众号后台回复“超高分辨率互作”获取文献合集
参考文献:
1.Swygert S G, Kim S, Wu X, et al. Condensin-dependent chromatin compaction represses transcription globally during quiescence[J]. Molecular Cell, 2019, 73(3): 533-546. e4.
2.Swygert S G, Lin D, Portillo-Ledesma S, et al. Chromatin fiber folding represses transcription and loop extrusion in quiescent cells[J]. bioRxiv, 2021: 2020.11. 24.396713.
3.Hansen A S, Hsieh T H S, Cattoglio C, et al. Distinct classes of chromatin loops revealed by deletion of an RNA-binding region in CTCF[J]. Molecular cell, 2019, 76(3): 395-411. e13.
4.Hsieh T H S, Cattoglio C, Slobodyanyuk E, et al. Resolving the 3D landscape of transcription-linked mammalian chromatin folding[J]. Molecular cell, 2020, 78(3): 539-553. e8.
 微信公众号
微信公众号
