
//
可变剪接(Alternative Splicing,AS),也叫选择性剪接,是指通过不同的剪接方式,选择性地包含或排除外显子和内含子,从而产生不同的mRNA剪接异构体的过程,是调节基因表达和产生蛋白质多样性和复杂性的重要机制。
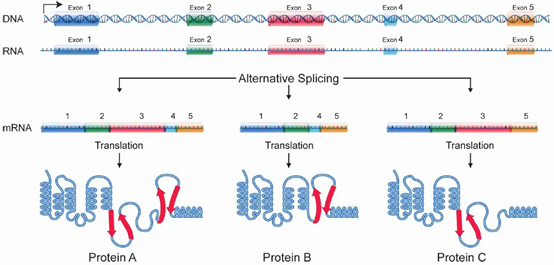
图1 可变剪接示意图
已有研究表明,可变剪接在生物过程中扮演重要角色。是在RNA水平调控基因表达的机制之一,使生物表型具有多样性和复杂性。
PacBio三代技术凭借其长读长和高准确度的优势,是研究AS的有利工具。基于此技术的三代全长转录组(Iso-seq)也已经在相关研究中被大量应用并利用其无须组装拼接、高准确度的特性,解析了许多生物学问题。今天小编也精选几篇相关研究,希望能为各位老师扩宽思路。
01
全长转录组测序揭示了不同胃癌类型可变剪接的多样性

发表期刊:Genome Biology
发表时间:2021年1月
研究技术:Iso-seq+RNA-seq
研究内容:
癌症的标志之一就是基因表达失调,但是现今大多数研究都只使用了RNA-seq来进行研究,但因为其读长的局限性解析并不全面。研究基于PacBio的长读长测序(Iso-seq)和基于illumina的RNA-seq全面调查了全球主要致死癌症之一的胃癌(GC)的转录情况。
研究对10种GC细胞进行了全长转录组分析,涵盖了4种主要的GC亚型。识别出了60,239个非冗余的全长转录本,其中超过66%的转录本是新发现。新发现转录本可能是每个GC亚型特有,表达水平较低,外显子较多且长度较长。在多种类型的AS情况中,大多数新转录本出现首位外显子跳跃,且表达水平越高,可变性越强。同时,研究检测到的25%的基因都存在启动子的变化,大多数启动子的变化也会对编码产生潜在影响,通过与TCGA中GC样本的对应,研究确定了几种与癌症相关的异构体。肿瘤特异性转录本往往会更大程度上改变蛋白质编码序列,研究利用了Iso-seq技术,为后续深入研究GC和其他肠道肿瘤提供了丰富的全长转录组资源。
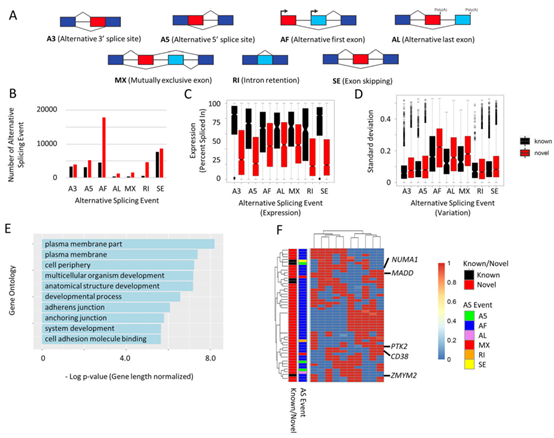
图2 可变剪接改变的类型
02
全长转录组助力乳腺癌研究

发表期刊:Science Advances
发表时间:2022年1月
研究技术:Iso-seq
研究内容:
肿瘤往往伴随着广泛的转录组变化,但癌症中不同亚型的可变剪切内容尚不清楚。研究基于PacBio的长度长测序,对得到的结果进行后续分析,进而识别和注释全长转录本并推断肿瘤的特异性剪接事件。研究识别出了数千种新转录本,30%出现了外显子改变,对蛋白质定位和功能存在潜在影响。使用omics数据集进行了进一步验证,确定了3059个乳腺肿瘤特异性剪接事件,包括35个与患者生存存在显著相关的AS。总的来说,研究证明了乳腺癌中存在此前未鉴定出的转录本和AS的复杂性、癌症亚型的特异性和临床相关性。
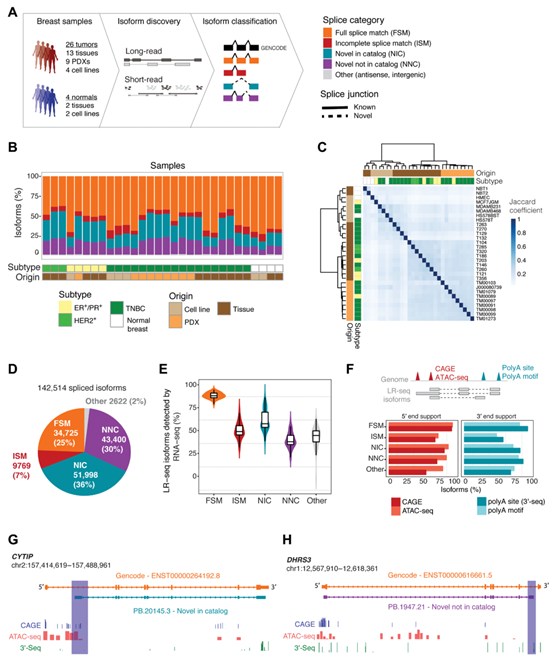
图3 Iso-seq可识别乳腺癌中新的转录本
03
Iso-seq助力人类和小鼠大脑皮层研究

发表期刊:Cell Reports
发表时间:2021年11月
研究技术:Iso-seq
研究内容:
可变剪接是重要的转录后调控机制,可以从单个mRNA前体中产生多个不同的mRNA,在中枢神经系统发育和功能中发挥着重要作用。研究使用Iso-seq检测人和小鼠大脑皮层中生成全长转录本序列。确定了大量现有基因组注释中不存在的新转录本,包括映射到新基因的转录本和包含多个基因组的融合转录本。
尽管某些基因的特点是物种之间存在显著差异,但了和小鼠皮层之间的转录多样性整体模式显示。研究还进一步确定了AS的发育变化,人类胎儿和成人皮质之间的转录本也存在不同。研究证实了皮质中选择性剪接的重要性,显著增加了转录多样性,并代表了大脑中基因调控的重要机制。
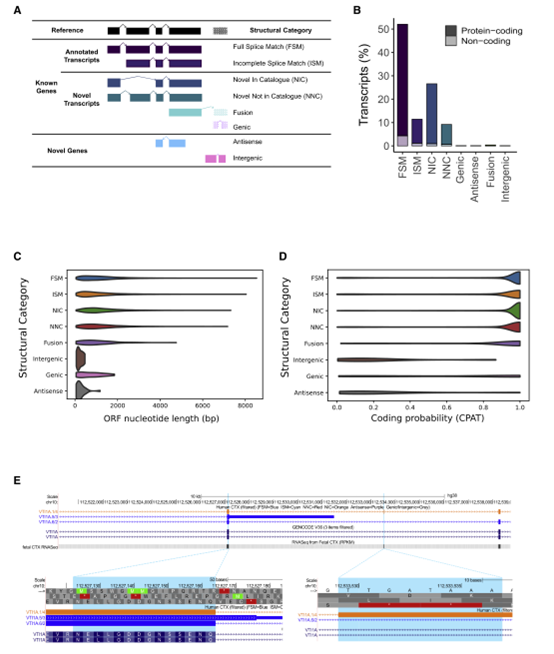
图 3 现有注释中大量未描述的转录本
参考文献:
1.Huang KK, Huang J, Wu JKL, et al. Long-read transcriptome sequencing reveals abundant promoter diversity in distinct molecular subtypes of gastric cancer.Genome Biol. 2021;22(1):44. Published 2021 Jan 22.
2.Veiga DFT, Nesta A, Zhao Y, et al. A comprehensive long-read isoform analysis platform and sequencing resource for breast cancer. Sci Adv. 2022;8(3):eabg6711.
3.Leung SK, Jeffries AR, Castanho I, et al. Full-length transcript sequencing of human and mouse cerebral cortex identifies widespread isoform diversity and alternative splicing. Cell Rep. 2021;37(7):110022.
 微信公众号
微信公众号
