
自人类T2T基因组发表以来,关于T2T基因组的算法、综述与物种应用变的越来越广泛,与之相对应的高分文章也越来越多。此外,PacBio HiFi+ONT超长测序的联合应用,也使得T2T基因组的构建越来越普遍化。基于此,小编特对近期的T2T相关物种文章、研究方法与前沿综述进行汇总,以飨读者。
1
近期发表T2T基因组的物种
(1)甘蔗叶枯病菌T2T基因组

Stagonospora tainanensis是甘蔗叶枯病的主要致病菌,该菌可造成甘蔗大面积的叶片早枯,显著降低甘蔗产量和蔗糖分。了解Stagonospora tainanensis的基因组结构,开发甘蔗叶枯病的基因型鉴定,对于甘蔗叶枯病防治至关重要。本研究中,结合ONT超长测序,研究者组装了T2T水平的Stagonospora tainanensis基因组,其基因组大小为38.25Mb,contig N50=2.86Mb;共注释得到12543个蛋白编码基因,重复序列含量为13.20%,BUSCO评估完整性为99.18%,这表明研究者构建了高质量的Stagonospora tainanensis基因组。此外,通过数据库注释及比较基因组学分析,研究者在Stagonospora tainanensis基因组中还鉴定到了2379个PHI、599个CAZys、248个膜转运蛋白、191个细胞色素P450酶、609个推测分泌蛋白和333个效应子。总之,本研究为甘蔗叶枯病的防治提供重要参考依据。

图1 甘蔗叶枯病菌T2T基因组
(2)苦瓜Mca-T2T基因组

苦瓜Mca(Momordica charantia L.var. abbreviate Ser.)是葫芦科苦瓜的变种,其果实比苦瓜果实小,果实成熟时果皮由绿色变为黄色/橙色,果肉由苦白色变为甜红色。苦瓜Mca即可食用,也可用于观赏。本研究中,研究者构建了苦瓜的T2T基因组,其11条染色体中有6条属于T2T水平,总基因组大小为295.6Mb,contig N50=25.4Mb,共包括19895个蛋白编码基因。共线性分析揭示了苦瓜果实质量的变化。通过高通量测序和代谢分析对转座酶可及染色质(A TAC)的检测表明,苦瓜糖苷和其他物质是Mca果肉的特征。转录组学和代谢组学联合分析揭示了Mca果皮色素积累和葫芦素生物合成的机制,为进一步研究Mca果实成熟提供了基础分子信息。
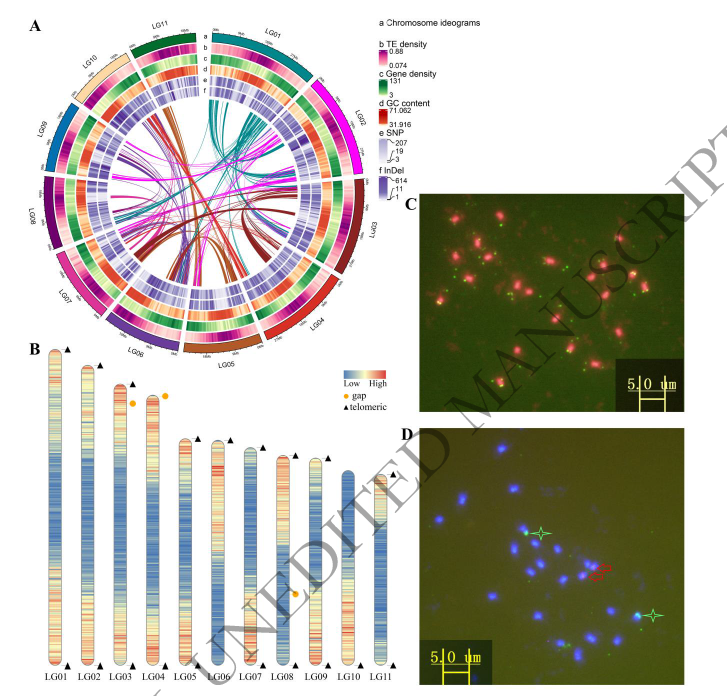
图2 苦瓜Mca-T2T基因组
(3)八倍体草莓T2T基因组

已有的八倍体草莓基因组Fragaria × ananassa是通过trio-binning的方式结合亲本数据进行组装的。本研究中,在无亲本的情况下,研究者通过HiFi和Hi-C测序,构建了八倍体草莓‘Florida Brilliance’ (FaFB2)的单倍型T2T基因组。两个单倍型的N50分别为23.7Mb和26.6Mb,具有很高的连续性。来自单倍型1和单倍型2的所有56条假染色体在5′和/或3′端均含有假定的端粒序列。通过遗传图谱、共线性分析、LTR指数、BUSCO评估、测序数据比对等方式证实了组装的草莓T2T基因组具有高质量和高完整性。结合二代和全长转录组数据,研究者在八倍体草莓中注释到了104099个基因。总之,T2T水平的Florida Brilliance基因组可为草莓基因组进化和基因功能的研究提供新见解。
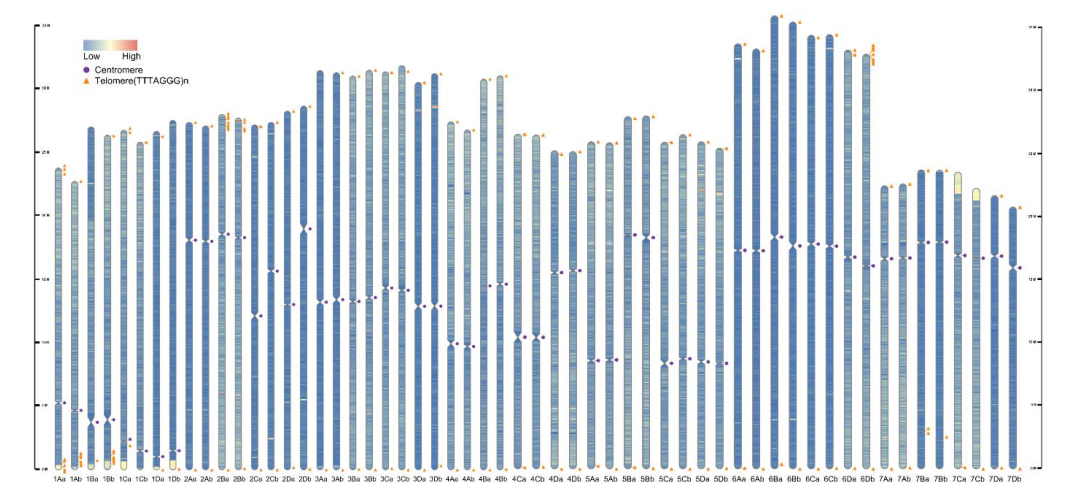
图3 八倍体草莓T2T基因组
(4)烟曲霉T2T基因组

致病性真菌烟曲霉(Aspergillus fumigatus)是真菌侵袭性和慢性疾病的主要病原菌,影响着全世界几千万人。目前临床上常用的烟曲霉菌参考基因组是Af293和A1163,但上述参考基因组缺乏着丝粒覆盖率、核糖体准确的重复序列以及染色体重排(如易位和反转)的全面注释。
本研究中,研究者使用PacBio和ONT测序,完成了两个烟曲霉CEA10(A1163的亲代分离物)及其后代A1160的T2T组装,组装的基因组大小为29.32Mb。研究者生成了CEA10的全长染色体组和全面的端粒到端粒覆盖率,以及A1160的近乎完整的基因组,包括核糖体重复序列和着丝粒序列,这些序列由长转座子元件组成。总之,这些高质量的T2T基因组将成为研究烟曲霉生物学、致病性和毒力的基础资源。

图4 烟曲霉T2T基因组的注释
(5)灵芝T2T基因组

灵芝属(Ganoderma)是一个典型的真菌类群,在森林生态系统中作为腐生生物和植物病原体发挥着关键作用,同时也是名贵的中药材。但高质量参考基因组的缺乏阻碍了灵芝物种的功能和进化基因组研究。
本研究中,通过PacBio、ONT和Hi-C测序,研究者构建了灵芝属10个高质量的参考基因组,包括6个T2T基因组。随后又对224份个体进行重测序,这些数据可以研究灵芝物种及其历史种群动态的谱系。基于全基因变异,揭示了灵芝物种中广泛存在的全基因组渗入现象。具有显著渗入信号的基因与应激反应、消化吸收和次级代谢产物合成有关,这些因素可能有助于环境适应和重要的生物组分代谢。CYP512U6是与灵芝三萜合成相关的CYP450家族中的一个重要功能基因,结合灵芝代谢组学分析,通过显著的导入和选择信号检测到该基因,表明古老的基因交换和最近的驯化都对灵芝次生代谢物的种类和含量有贡献。综上,本研究组装的基因组资源、变异图谱、转录和代谢数据,对灵芝属的进化研究至关重要。
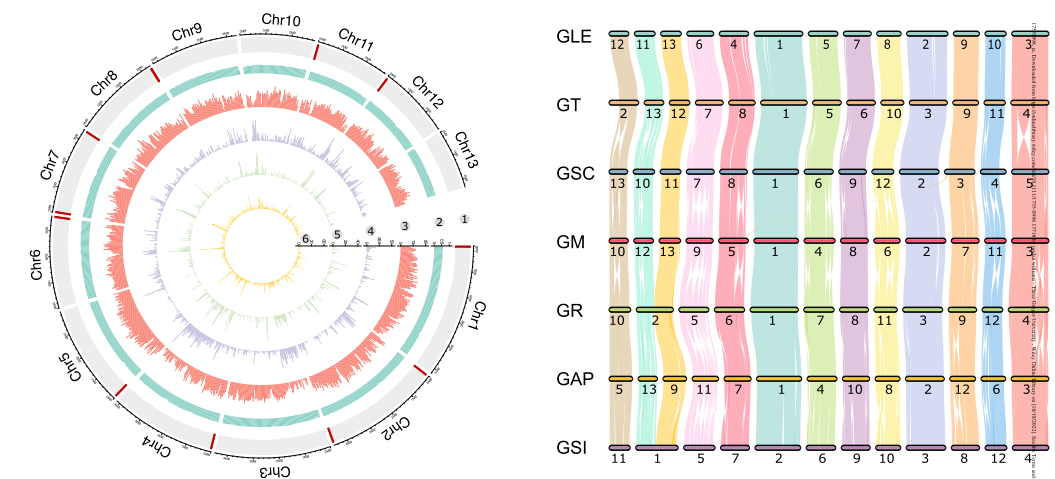
图5 灵芝属的基因组特征及共线性分析
2
近期发表的T2T算法

最近发表的人类T2T基因组对人类医学研究产生了广泛影响,但其是从几乎纯合的细胞系中衍生出来的,缺少杂合性。人类泛基因组参考联盟,其目的是创建高质量、低成本、分型的二倍体T2T基因组。为此,研究者评估了23种组装方法组成的基因组,对60多个指标进行了广泛评估,形成了一种结合不同策略以获得最高分数的方法。
得分比较高的方法建议在组装过程中,使用母亲-父亲-后代三组数据来解析后代单倍型,同时合并不同类型的序列数据和组装工具。此外,该研究主要有两个结果。首先,它确定了不同最先进的组装算法和工作流程的优点和缺点,使研究人员能够选择合适的方法来使用他们的数据,并使开发人员能够解决缺点;其次,这项研究使HPRC能够确定并应用最佳的方法来进行人类基因组组装。
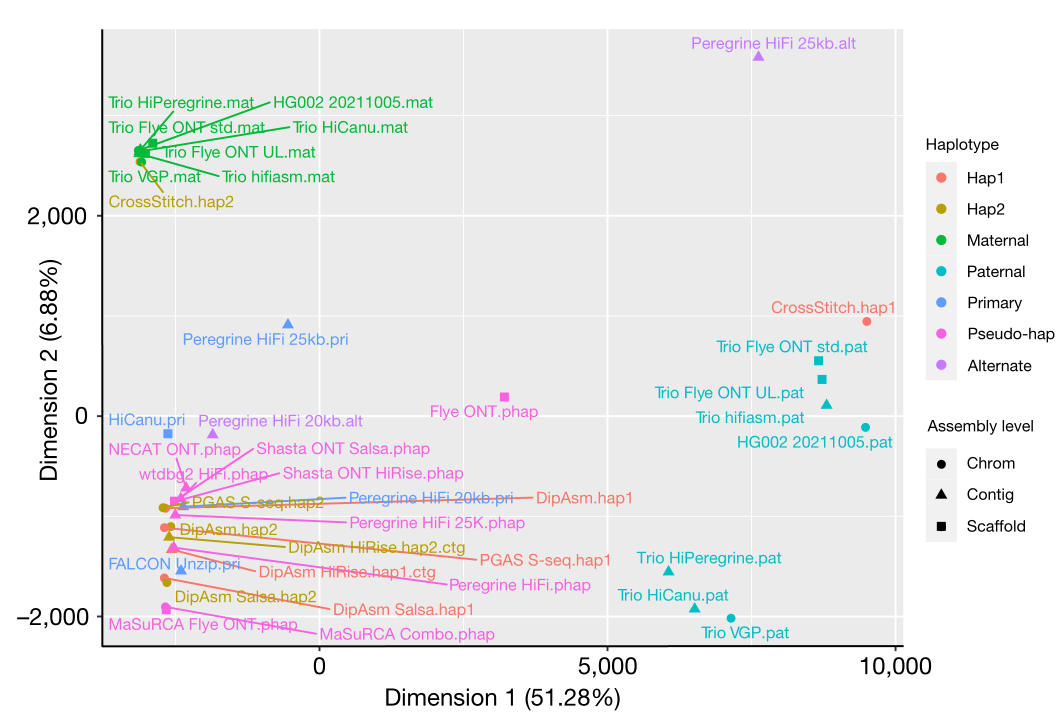
图6 不同组装方法间的相关性评估
3
近期发表的T2T综述

植物基因组编码了植物如何在漫长的进化历史中应对复杂环境的奥秘。在过去的20年里,快速发展的技术使得数百个植物草图或参考基因组得以解码。植物的多样性、多倍体和杂合性使得产生高质量的植物基因组组合在技术上具有挑战性和耗时性。最近发明的ultra-long测序技术已经达到了一个里程碑,几个植物基因组已经无间隙地组装成端粒到端粒。端粒到端粒(T2T)基因组是指具有高基因组准确性、高连续性和高完整性的高质量完整基因组。随着完整的人类基因组和拟南芥基因组的发布,完整的T2T物种基因组时代已经到来。在这篇综述中,我们总结了基于新兴ultra-long测序技术的无间隙植物基因组的历史。我们讨论如何依靠靶向基因组测序和组装技术来减少gap。然而,在超大、多倍体和不稳定的基因组中仍然存在许多挑战。尽管如此,这些完整的基因组已经提供了前所未有的信息,这必将加深我们对植物基因组的理解和对更多功能序列的探索。通过利用完整的基因组,可以对一系列重要基因进行注释,这将有助于实现作物物种基因组设计的目标。
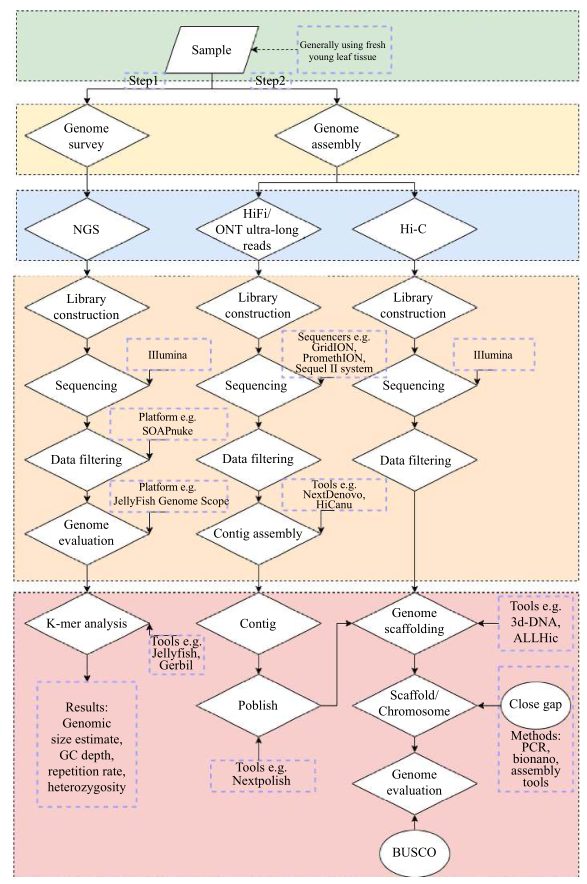
图7 T2T基因组的组装流程
参考文献:
[1] Xu F, Li X, Ren H, et al. The First Telomere-to-Telomere Chromosome-Level Genome Assembly of Stagonospora tainanensis Causing Sugarcane Leaf Blight[J]. Journal of Fungi, 2022, 8(10): 1088.
[2] Fu A, Zheng Y, Guo J, et al. Telomere-to-telomere genome assembly of bitter melon (Momordica charantia L. var. abbreviata Ser.) reveals fruit development, composition and ripening genetic characteristics[J]. Horticulture Research, 2022.
[3] Han H, Barbey C R, Fan Z, et al. Telomere-to-Telomere and Haplotype-Phased Genome Assemblies of the Heterozygous Octoploid′ Florida Brilliance′ Strawberry (Fragaria× ananassa)[J]. bioRxiv, 2022.
[4] Bowyer P, Currin A, Delneri D, et al. Telomere-to-telomere genome sequence of the model mould pathogen Aspergillus fumigatus[J]. Nature communications, 2022, 13(1): 1-7.
[5] Jiang N, Li Z, Dai Y, et al. Massive genome investigations reveal insights of prevalent introgression for environmental adaptation and triterpene biosynthesis in Ganoderma[J]. Molecular Ecology Resources, 2022.
[6] Jarvis E D, Formenti G, Rhie A, et al. Semi-automated assembly of high-quality diploid human reference genomes[J]. Nature, 2022: 1-13.
[7] Zhou Y, Zhang J, Xiong X, Cheng Z, Chen F. 2022. De novo assembly of plant complete genomes. Tropical Plants 1:7 doi: 10.48130/TP-2022-0007
 微信公众号
微信公众号
